引言
如果酶具有协同亚基,则酶速率与底物浓度关系的曲线将呈现S形。Prism提供了一个经验方程,用于拟合S形底物-速率曲线。有关基于别构模型的其他方法,请参阅酶动力学方面的进阶书籍。
如何输入数据
创建一个 XY 数据表。将底物浓度输入 X 列,酶速率输入 Y 列。如果有多个实验条件,请将第一个条件放在 A 列,第二个放在 B 列,依此类推。
输入数据后,点击“分析”,选择“非线性回归”,选择“酶动力学方程”面板,然后选择“变构S形酶动力学”。
模型
Y=Vmax*X^h/(Khalf^h + X^h)
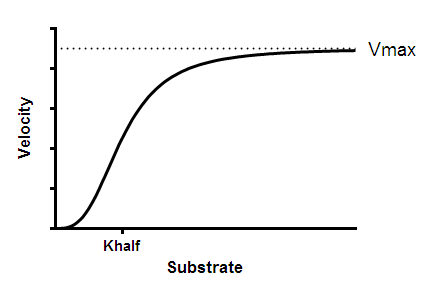
参数解读
Vmax 是酶的最大反应速率,单位与 Y 相同。它是酶在极高底物浓度下外推得到的反应速率,因此几乎总是高于实验中测得的任何反应速率。
Khalf 是产生半最大酶速率的底物浓度,即 EC50。
h 是 Hill斜率。当 h=1 时,该方程与标准米氏-门登方程完全一致。当 h 大于 1.0 时,由于正协同作用,曲线呈 S 形。变量 h 不一定等于交互作用的结合位点数,但其值不能超过交互作用位点数。可将 h 视为曲线陡峭程度及协同作用存在与否的经验性衡量指标。
Kprime 与 Km 相关。其计算公式为 Khalf^h,且单位与 X 相同。
方程的另一种形式
该方程的另一种形式(参见下文所引 Copeland 博士著作中的方程 5.47)适用于 Kprime。
Y=Vmax*X^h/(Kprime + X^h)
请注意,此方程中的 Kprime 等于 Prism 内置方程中的 Khalf^h。这两个模型生成的曲线完全相同,只是参数的报告方式不同。Prism 同时报告 Kprime 和 Khalf。